Die oxygene Fotosynthese der Cyanobakterien ist ein abgeleitetes Merkmal
Cyanobakterien waren vor spätestens 2,7 Milliarden Jahren die ersten Lebewesen, die eine Fotosynthese durchführten, die Sauerstoff produzierte, die sogenannte oxygene Fotosynthese.
Der Fotosyntheseapparat der Cyanobakterien
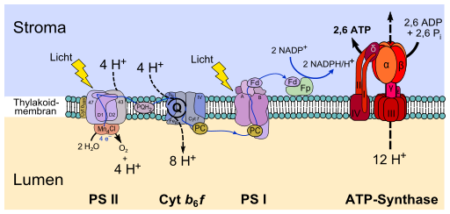
Der modulare Fotosyntheseapparat für diese oxygene Fotosynthese besteht aus fünf Multiproteinkomplexen: Lichtsammel-Antennenkomplex, den Fotosystemen I und II (PS I und PS II), dem Cytochrom b6-f-Komplex (Cytb6f) und der ATP-Synthase. Hinzu kommen Enzyme für die Chlorophyll- und Carotenoidbiosynthese, die CO2-Fixierung und den Elektronentransport.

Die Thylakoidmembran eines Chloroplasts einer pflanzlichen Zelle, die oxygene Fotosynthese betreibt.
Die mosaikartige Evolution der Fotosynthese
Es gibt neben den Cyanobakterien1 fünf Bakterienfamilien, die Fotosynthese betreiben: Purpurbakterien, grüne Nichtschwefelbakterien, Heliobakterien, grüne Schwefelbakterien und Acidobakterien. Bei diesen anoxygenen Fotosynthesen entsteht aber kein Sauerstoff. Es ist bisher nur klar, dass die anoxygene Fotosynthese vor der oxygenen Fotosynthese entstand, es ist aber nicht klar welche dieser fünf Bakterienfamilien die erste war die anoxygene Fotosynthese betrieb.
Nur die Cyanobakterien besitzen die Fotosysteme I und II, die anderen fotosynthetischen Bakterien besitzen jeweils nur ein Reaktionszentrum, das evolutionär entweder mit dem Fotosystem I oder mit dem Fotosystem II verwandt ist. Was das Verständnis der Evolution der Fotosyntheseapparate enorm erschwert ist deren modularer Aufbau: die fünf Multiproteinkomplexe und die Enzyme haben jeweils ihre eigene Evolutionsgeschichte. Die Biologen sprechen daher von einer mosaikartigen Evolution der Fotosynthese. Die jeweils etwas mehr als 100 Gene, die für die Proteine der Fotosynthesapparate codieren, haben ähnliche DNA-Sequenzen, sodass Forscher glauben, dass sie von gemeinsamen Urgenen abstammen. Da Cyanobakterien, die einzigen Bakterien sind, die zur oxygenen Fotosynthese fähig sind, möchten Evolutionsbiologen wissen wie und wann sie die dafür notwendigen Gene erwarben.
Grundlagen der phylogenetischen Systematik
Um diese Fragen zu beantworten, benutzten Forscher der Universität Queensland in St. Lucia, Australien und des California Institute of Technology in Pasadena, USA eine phylogenetische Analyse [1]. Bei der phylogenetischen Analyse ordnen Wissenschaftler Lebewesen in Stammbäume ein, um die stammesgeschichtliche Entwicklung dieser Lebewesen bildlich darzustellen. Dabei stellen sie die Stammbäume auf der Grundlage von vererbbaren Merkmalen auf. Daher verwendet die moderne Phylogenetik auch DNA-Sequenzen, um mit Algorithmen der Bioinformatik den Verwandtschaftsgrad zwischen Arten zu bestimmen.
Wichtig für die phylogenetische Analyse ist das neu entstandene Merkmal einer Art, das sie von einer anderen verwandten Art unterscheidet. Stammbaumforscher bezeichnen ein solches Merkmal als abgeleitetes oder autapomorphes Merkmal. Ein abgeleitetes Merkmal stellt das Alleinstellungsmerkmal einer Art dar. Demgegenüber steht das ursprüngliche oder plesiomorphe Merkmal. Ursprüngliche Merkmale sind bereits vor der jeweils betrachteten Stammeslinie entstanden und haben sich nicht im Laufe der Zeit verändert. Sie sind also bei mehreren Arten zu finden.
Ein Merkmal gilt dann sicher als abgeleitet, wenn es innerhalb des eigenen Taxons homolog vorhanden ist und bei allen Schwestergruppen nicht vorhanden ist. Ein Beispiel: Das Taxon der Fluginsekten (Pterygota) hat als begründendes abgeleitetes Merkmal zwei Flügelpaare. Die Vorfahren der heutigen Fluginsekten waren flügellos. Die Flügellosigkeit der Urinsekten (Apterygota) und übrigen Gliederfüßer (Arthropoda) wie Spinnen (Arachnida), Tausendfüßern (Myriapoda), Krebsen (Crustacea) ist ein ursprüngliches Merkmal. Betrachtet man die Fluginsekten für sich, ist das Merkmal „zwei Flügelpaare“ ein ursprüngliches Merkmal! Erst deren weitere Veränderung, z. B. Umwandlung des vorderen Paares zu Flügelklappen bei allen Käfern (Coleoptera) stellt ein neues abgeleitetes Merkmal dar, welches nun innerhalb der Fluginsekten das Taxon der Käfer begründet. Bei der Suche nach abgeleiteten Merkmalen beziehen die Stammbaumforscher auch das Fehlen von Merkmalen (Negativmerkmale) in ihre Argumentation mit ein. Ein Beispiel: Die Flügellosigkeit der Urinsekten ist ein ursprüngliches Negativmerkmal die Flügellosigkeit der Flöhe (Siphonaptera), die zu den Fluginsekten gehören, ein abgeleitetes.
Evolutionsbiologen möchten wissen, welches die ursprünglichen und welches die abgeleiteten Merkmale sind, da sie so bestimmen können, in welche Richtung die Evolution der Merkmale innerhalb eines Taxons verlief. Dabei untersuchen sie zusätzlich zu den eigentlich interessierenden Taxa eine weitere Gruppe, die nach Möglichkeit nah mit den zu analysierenden Taxa verwandt ist aber auf gar keinen Fall in eines dieser Taxa gehört oder Schwestergruppe eines dieser Taxa ist. Eine solche Gruppe wird als Außengruppe bezeichnet, die Taxa, für die man die Verwandtschaftsbeziehungen wissen möchte als Innengruppe.
Treten in der Innengruppe für ein Merkmal die Ausprägungen a und b auf, so ist allein aufgrund dieser Feststellung nicht entscheidbar, welche Ausprägung die ursprüngliche ist. Wird nun in der Außengruppe das gleiche Merkmal untersucht und festgestellt, dass hier die Ausprägung a vorhanden ist, so kann mit hoher Wahrscheinlichkeit davon ausgegangen werden, dass a der ursprüngliche Zustand ist.
Phylogenetik der Fotosynthese
Die Fähigkeit zur oxygenen Fotosynthese ist ein physiologisches vererbbares Merkmal. Bis vor vier Jahren besaßen alle bis dahin bekannten Klassen von Cyanobakterien dieses Merkmal. Da aber weder die Vorfahren der Cyanobakterien noch deren nächsten Verwandten bekannt waren, konnten die Wissenschaftler nicht sagen, ob es sich bei der oxygenen Fotosynthese der Cyanobakterien um ein ursprüngliches oder ein abgeleitetes Merkmal handelt.
Das Bild änderte sich 2013 mit der Entdeckung der Melainabacteria, einer Gruppe von nichtphotosynthetischen Cyanobakterien, die eng mit den photosynthetischen Cyanobakterien verwandt sind. 2016 entdeckten die Bakteriologen eine weitere Gruppe von nichtphotosynthetischen Cyanobakterien, die Sericytochromatia. Oxyphotobacteria, Melainabacteria und Sericytochromatia bilden eine monophyletische Gruppe, die eine jüngste gemeinsame Stammform und auch alle Untergruppen, die sich von dieser Stammform herleiten, umfasst, jedoch keine andere Gruppe.
Die Biochemiker vermuteten, dass der gemeinsame Vorfahre dieser drei Gruppen oxygene Fotosynthese betrieb und diese Fähigkeit bei den Melainabacteria und den Sericytochromatia im Laufe der Evolution verloren gegangen ist, weil die Fotosynthesegene durch Mutationen geschädigt wurden oder einige ganz verloren gingen. Die Forscher sequenzierten daher insgesamt 41 Bakteriengenome der Melainabacteria (38) und Sericytochromatia (3), um Überbleibsel von jenen Fotosynthesegenen zu finden.
Sie wurden enttäuscht: Sie fanden keine Fotosynthesegene. Die Genetiker vermuten daher, dass der gemeinsame Vorfahr dieser drei Gruppen auch keine Fotosynthesegene besaß und deshalb nicht zur Fotosynthese fähig war. Aber wie und wann haben dann die Oxyphotobacteria ihre Fotosynthesegene erworben?
Durch horizontalen Gentransfer, nachdem sich die Oxyphotobacteria von den Melainabacteria getrennt hatten. Das bedeutet, die oxygene Fotosynthese der Oxyphotobacteria ist ein abgeleitetes Merkmal.
Fußnoten
1. Blaualgen ist ein Begriff, der heute leider noch oft für Cyanobakterien verwendet wird. Das liegt daran, dass sie früher zu den Algen (Phycophyta) gerechnet wurden und als Klasse Blaualgen (Cyanophyceae) geführt wurden. Algen sind jedoch Eukaryoten und keine Bakterien. Die Vorsilbe cyano leitet sich vom griechischen Wort kyanos für Blau ab. Einige Cyanobakterien enthalten blaues Phycocyanin und ihre Farbe ist deshalb blaugrün. Darum wurden sie „Blaualgen“ genannt und diese Bezeichnung wurde für alle Cyanobakterien verwendet – auch für diejenigen, die kein Phycocyanin enthalten und nicht blaugrün gefärbt sind.
Weiterführende Literatur
Blankenship, R. E. (2017) How Cyanobacteria went green Science. 355: 1372-1373


Pingback:[SciLogs] Die oxygene Fotosynthese der Cyanobakterien ist ein abgeleitetes Merkmal
Man könnte in einige Nutzpflanzen die Gene für die Synthese der Phycobiline einbauen, damit ein größerer Bereich des Spektrums in der Grünlücke des Chlorophylls genutzt wird.
Dann hätte man schwarzen Salat, und den viel schneller.
Joe Dramiga schrieb (7. Juni 2017):
> Die Fähigkeit zur oxygenen Fotosynthese ist ein physiologisches vererbbares Merkmal […] der Cyanobakterien
> Die jeweils etwas mehr als 100 Gene, die für die Proteine der Fotosyntheseapparate codieren, haben ähnliche DNA-Sequenzen, sodass Forscher glauben, dass sie von gemeinsamen Urgenen abstammen.
Verstehe ich das recht:
Sind alle mehr als 100 Gene, die für die Proteine der (modernen) Fotosyntheseapparate codieren, einander so ähnlich, dass sie von einer einzigen Fotosynthese-“Urgen“-Form abstammen könnten ?
Oder wie viele verschiedene, geeignet deutlich unterscheidbare “Urgen“-Formen lägen den entsprechenden modernen “mehr als 100 Genen” zugrunde ?
> Entdeckung der Melainabacteria, einer Gruppe von nichtphotosynthetischen Cyanobakterien, die eng mit den photosynthetischen Cyanobakterien verwandt sind.
> Die Forscher sequenzierten […] Bakteriengenome der Melainabacteria (38)
> […] Sie fanden keine Fotosynthesegene.
Beruht die Charakterisierung des Grades der Verwandschaft zwischen photosynthetischen Cyanobakterien und Melainabacteria als “eng” auf einem Vergleich ihrer Genome, und zwar offensichtlich insbesondere derjenigen Gene, die nicht für die Proteine der Fotosynthesaepparate codieren ?
Wie viele Gene haben photosynthetische Cyanobakterien bzw. Melainabacteria denn überhaupt, etwa ?
> Aber wie und wann haben dann die Oxyphotobacteria ihre Fotosynthesegene erworben?
> Durch horizontalen Gentransfer, nachdem sich die Oxyphotobacteria von den Melainabacteria getrennt hatten.
Sofern die genannten “mehr als 100 Gene, die für die Proteine der [modernen] Fotosyntheseapparate codieren” von einer einzigen “Urgen“-Form abstammen könnten,
wäre es nicht stattdessen z.B. vorstellbar, dass sich die Melainabacteria dadurch von den Oxyphotobacteria trennten, dass erstere das (eine) Fotosynthese-“Urgen” hinreichend vollständig einbüßten, das in gemeinsamen Vorfahren noch vorhanden war ?
Sind alle mehr als 100 Gene, die für die Proteine der (modernen) Fotosyntheseapparate codieren, einander so ähnlich, dass sie von einer einzigen Fotosynthese-„Urgen„-Form abstammen könnten?
Nein, sie sind einander nicht so ähnlich. Das habe ich ja im Text mit dem Hinweis auf den modularen Aufbau und die mosaikartige Evolution andeuten wollen.
Damit ist nicht gemeint, dass z. B. in Cyanobakterien die Gene für den Lichtsammel-Antennenkomplex und die Gene für die ATP-Synthase ähnliche DNA-Sequenzen haben und auf ein gemeinsames Urgen zurückgehen.
Sondern damit ist gemeint, dass z. B. die Gene für das PSI in grünen Schwefelbakterien (dort PSC genannt) und die Gene für das PSI in Heliobakterien (dort PSH genannt) ähnliche DNA-Sequenzen haben und von gemeinsamen PSI-Urgenen abstammen. Bei den anderen vier Multiproteinkomplexen und den Enzymen sollte man sich das analog so denken.
Oder wie viele verschiedene, geeignet deutlich unterscheidbare „Urgen„-Formen lägen den entsprechenden modernen „mehr als 100 Genen“ zugrunde?
Wie viele verschiedene Urgene den entsprechenden modernen Fotosynthesegenen zugrunde liegen, weiß man nicht.
Beruht die Charakterisierung des Grades der Verwandschaft zwischen photosynthetischen Cyanobakterien und Melainabacteria als „eng“ auf einem Vergleich ihrer Genome, und zwar offensichtlich insbesondere derjenigen Gene, die nicht für die Proteine der Fotosynthesaepparate codieren?
Ja.
Wie viele Gene haben photosynthetische Cyanobakterien bzw. Melainabacteria denn überhaupt, etwa?
Melainabacteria haben etwa 1800 Gene, die photosynthetischen Cyanobakterien haben zwischen 2700 und 3600 Gene.
Sofern die genannten „mehr als 100 Gene, die für die Proteine der [modernen] Fotosyntheseapparate codieren“ von einer einzigen „Urgen„-Form abstammen könnten, wäre es nicht stattdessen z.B. vorstellbar, dass sich die Melainabacteria dadurch von den Oxyphotobacteria trennten, dass erstere das (eine) Fotosynthese-„Urgen“ hinreichend vollständig einbüßten, das in gemeinsamen Vorfahren noch vorhanden war?
Wenn es so ein einziges Urgen gäbe, wäre so eine Szenario vorstellbar.
Joe Dramiga schrieb (9. Juni 2017 @ 15:46):
> […] dass z. B. die Gene für das PSI in grünen Schwefelbakterien (dort PSC genannt) und die Gene für das PSI in Heliobakterien (dort PSH genannt) ähnliche DNA-Sequenzen haben und von gemeinsamen PSI-Urgenen abstammen. Bei den anderen vier Multiproteinkomplexen und den Enzymen sollte man sich das analog so denken.
Danke für die Erläuterung.
> Wie viele verschiedene Urgene den entsprechenden modernen Fotosynthesegenen zugrunde liegen, weiß man nicht.
Aufgrund der im obigen SciLogs-Artikel genannten Anzahl: …
Joe Dramiga schrieb (7. Juni 2017):
> Der modulare Fotosyntheseapparat für diese oxygene Fotosynthese besteht aus fünf Multiproteinkomplexen […] Hinzu kommen Enzyme für die Chlorophyll- und Carotenoidbiosynthese, die CO2-Fixierung und den Elektronentransport.
… lägen wohl ca. (höchstens?) neun unterscheidbare “Urgene” zugrunde.
Wenn nun genau nur eine dieser neun (“Ur“-)”DNA-Sequenzen” in einem Bakterium derart beschädigt worden wäre, dass es keine Photosynthese mehr ausführen konnte, aber dennoch überlebte bzw. fortpflanzungsfähige Nachkommen hätte —
über wie viele Generationen von Nachkommen kann erwartet werden, dass Überbleibsel der (anfänglich noch vorhandenen) “Fotosynthesegene” mit den im Beitrag genannten Verfahren noch auffindbar/erkennbar wären?
Multiproteinkomplex bedeutet, dass der Komplex aus vielen Proteinen besteht. Der Multiproteinkomplex PSII von Pflanzen z. B. enthält 30 Proteine. An der Biosynthese des Chlorophylls z. B. ist auch nicht nur ein Enzym beteiligt, sondern mehrere Enzyme, da dafür mehrere biochemische Reaktionen katalysiert werden müssen. Es liegen also mehr als neun unterscheidbare “Urgene” für diese vielen Proteine zugrunde.
Bezüglich deines Szenarios – nach wie vielen Generationen von Nachkommen man noch erwarten kann Überbleibsel dieser Fotosynthesegene im Genom zu finden. Ich weiß es nicht.
Joe Dramiga schrieb (12. Juni 2017 @ 16:06):
> Multiproteinkomplex bedeutet, dass der Komplex aus vielen Proteinen besteht. […]
Oh, natürlich! Meine obige (12. Juni 2017 @ 10:19) Abschätzung von “ (höchstens?) neun unterscheidbaren „Urgenen“” war inkorrekt; stattdessen, bezogen auf die im SCiLog-Beitrag genannten “jeweils etwas mehr als 100 Gene, die für die Proteine der [modernen, aus 5 Komplexen und ca. 4 Enzymen bestehenden] Fotosynthesapparate codieren“,
wäre von (höchstens?) ca. 100 unterscheidbaren „Urgenen“ auszugehen, die “den Ur-Fotosynthesapparat” kodierten.
(Unabhängig davon, ob diese „Urgene“ in einem vermeinlichen gemeinsamen Vorfahren der drei Cyanobakteriengruppen vorlagen, oder in einer vermeintlichen anderen Organismus-Gruppe, von dem sie horizontal transferiert worden wären.)
> [Wenn nun genau nur eines dieser ca. 100 Fotosynthese-„Urgene“ derart beschädigt worden wäre, dass der Betroffene keine Fotosynthese mehr ausführen konnte, aber dennoch überlebte bzw. fortpflanzungsfähige Nachkommen hätte, denen die eventuell noch vorhandenen Gen-Überreste ebenfalls nicht mehr zur Fotosynthese dienen könnten — ]
> nach wie vielen Generationen von Nachkommen man noch erwarten kann, Überbleibsel dieser Fotosynthesegene im Genom zu finden. Ich weiß es nicht.
Je größer die erwartete Zahl wäre, desto überzeugender könnte die im Beitragstitel vorweggenommene Schlussfolgerung (“Die oxygene Fotosynthese der Cyanobakterien ist ein abgeleitetes Merkmal“) sein.
Was wurde eigentlich aus den Chloroxybakterien, die so vor 20 oder 30 Jahren als eigenständige Gruppe mit oxygener Fotosynthese neben den Cyanobakterien geführt wurden? Hat man die bei den Cyanobakterien eingemeindet?
Die Chloroxybakterien (Chloroflexaceen) gehören zu den Grünen Nichtschwefelbakterien und betreiben eine anoxygene Fotosynthese.
In “Die fünf Reiche der Organismen” von Lynn Margulis und Karlene Schwartz, erschienen im Verlag Spektrum der Wissenschaft (1989, amerik. Original 1982), steht das aber anders. Da liest man:
“[…] als ihre Photosynthese der allgemeinen Reaktionsgleichung für grüne Organismen […] folgt. […] Tatsächlich ähneln sie den photosynthetisch aktiven Zellorganellen echter Grünalgen und Pflanzen, den Chloroplasten. Doch wegen ihrer eindeutig prokaryotischen Zellorganisation und weil sie grüne Sauerstoffproduzenten sind, schlagen wir für dieses Phylum die Bezeichnung Chloroxybacteria vor. Im Unterschied zu allen anderen photosynthetisch aktiven Bakterien, aber genau wie Grünalgen und höhere Pflanzen, besitzen die Chloroxybakterien neben Chlorophyll a auch Chlorophyll b.”
Als einzige bekannte Gattung des Phylums wird in dem Buch Prochloron angegeben, und wie ich jetzt bei Wikipedia gelesen habe, wird das heute den Cyanobakterien zugeschlagen.
Diesen Widerspruch kann ich leider nicht auflösen. Ich kenne die Arbeiten nicht, die die damalige Einteilung von Margulis und Schwartz begründen, aber ich weiß, dass spätestens seit der Jahrtausendwende die Chloroxybakterien in der Taxonomie einen neuen Platz bekamen. Ich vermute, dass dieses Umdenken auf Ergebnisse zurückgeht, die mit neuen molekularbiologischen Methoden erzielt wurden. Wenn ich mir die Lebensbedingungen dieser Bakterien anschaue, bezweifele ich, dass der Sauerstoff den diese Bakterien produzieren sollen wirklich aus der Fotosynthese kommt. Wenn sie überhaupt Sauerstoff produzieren, nehme ich an, kommt er aus einem anderen Stoffwechselweg.
Hallo Joe!! Ich schätze ihre Beiträge wirklich sehr!!! Willkommen in Deutschland (ah Köln) 🙂 🙂 LG aus Hamburg
Vielen Dank! Das freut mich! Viele Grüße aus Köln
Zitat:
Es waren die Heliobakterien und Heliobacterium modesticaldum scheint das einfachste Photosystem zu haben, welches zudem Hinweise auf den gemeinsamen Ursprung von Photosystem I und II gibt. Dies liest man im Quanta-Artikel Simple Bacteria Offer Clues to the Origins of Photosynthesis Zudem wurden Hinweise gefunden, dass die oxygene Photosynthese schon früh angelegt war und zwar bevor dieCyanobakterien auftauchten.
Danke für den Link zum Quanta-Artikel! Eine weitere Wissenslücke ist anscheinend geschlossen.